非监督学习
- 监督学习,它的特点是对已知样本产生的结果是有预期的,因此我们可以对样本进行标记,Training Set 可以表示为${(x^{(1)},y^{(1)}),(x^{(2)},y^{(2)}),…,(x^{(m)},y^{(m)}) }$
- 非监督性学习对样本产生的结果是无法预期的,因此无法对样本数据进行标,Training Set 可表示为${x^{(1)} x^{(2)},…,x^{(m)} }$,非监督学习要做的是在这些无标注的数据中寻找某种规则或者模式。比如将数据归类,也叫做聚类( Clustering )就是一种非监督学习算法
K-Means 算法
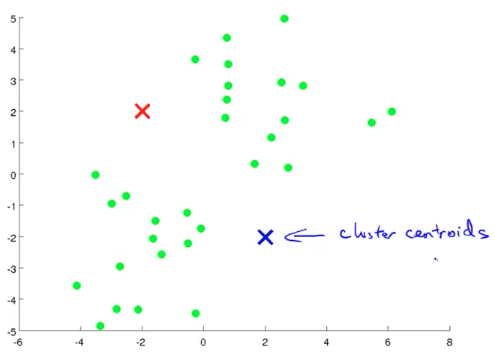
K-Means 是解决分类问题的一种很常用的迭代算法,具体步骤如下(以 K=2 为例)
- 在数据集中随机初始化两个点(红蓝叉),作为聚类中心(Cluster Centroid)
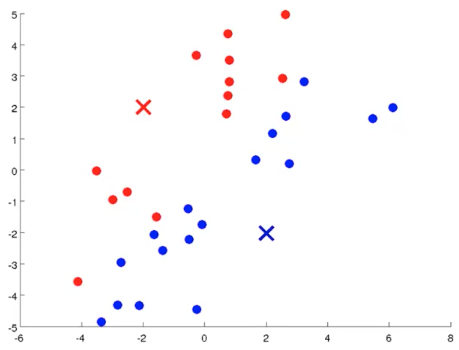
- 对样本进行簇分配(Cluster Assignment):对数据集中的所有样本计算到聚类中心的距离,按照样本据某个中心点距离远近进行归类
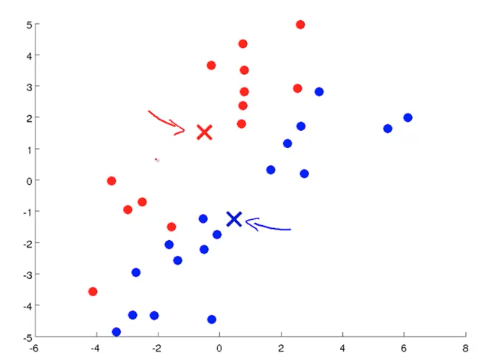
- 移动聚类中心 (Move Centroid): 对分类好的样本,求平均值,得到新的聚类中心
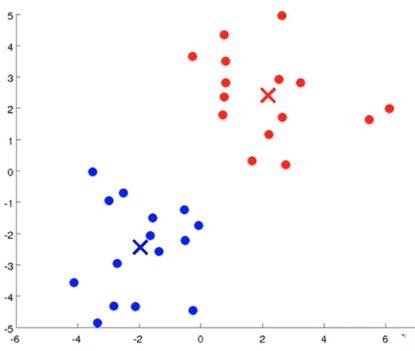
- 重复上述两个步骤,直到中心点不再变化
K-Means 函数的输入有两个参数:聚类数量 K 和训练集(默认$x_{0}=0$ )
随机初始化 K 个聚类中心点:$\mu_{1},\mu_{1}…,\mu_{k}$
Repeat{
$\text{for} \quad i=1 \quad \text{to} \quad m$
$\quad c^{(i)}:=\min_{k} |x^{(i)}-\mu_{k} |^{2}$//index of cluster(1,2,…K) to which example $x^{(i)}$ is currently assigned
$\text{end}$
$\text{for} \quad k=1 \quad \text{to} \quad K$
$\quad \mu_{k}:=\text{average(mean) of points assigned to cluster k}$
</br>
$\text{end}$
}
- 第一步的 Octave 实现为:
function idx = findClosestCentroids(X, centroids)
% Set K
K = size(centroids, 1);
% You need to return the following variables correctly.
idx = zeros(size(X,1), 1);
for i=1:size(X,1)
d_min=Inf;
for k=1:K
d=sum((X(i,:)-centroids(k,:)).^2); %这一步也可以用向量化实现
%
% diff = X(i, :)'-centroids(k, :)';
% d = diff'*diff;
%
if d<d_min
d_min=d;
idx(i)=k;
end
end
end
end
- 第二步的 Octave 实现为:
function centroids = computeCentroids(X, idx, K)
% Useful variables
[m n] = size(X);
centroids = zeros(K, n);
for k=1:K
num=0;
sum=zeros(1,n);
for i=1:m
if (k==idx(i))
sum=sum + X(i,:);
num=num+1;
end
end
centroids(k,:)= sum/num;
end
end
- K-Means 的优化目标函数为:找到$c^{(1)},…,c^{(m)},…,\mu_{1},…,\mu_{k}$使$J$最小:
- 其中 - $c^{(i)}$:样本$x^{(i)}$被分配到某个聚类的 index 值,例如:$x^{(i)} \to 5$,则$c^{(i)}=5$ - $\mu_{k}$:聚类中心点 - $\mu_{c^{(i)}}$:样本$x^{(i)}$被分配到某个聚类的中心点,例如:$x^{(i)} \to 5$,$c^{(i)}=5$,$\mu_{c^{(i)}}=\mu_{5}$
- J 也叫做Distortion Function,在实际求解上,参照上一节提供的步骤运算更好理解。
前面提到了在进行 K-Means 运算之前要先随机初始化 K 个聚类中心点:$\mu_{1},\mu_{1}…,\mu_{k}$($K<m$),通常的做法是在训练样本中随机选取$K$个样本作为$\mu_{1},\mu_{1}…,\mu_{k}$的值,即$\mu_{1}=x^{(i_{1})},\mu_{2}=x^{(i_{2})},\cdots,\mu_{k}=x^{(i_{k})}$。如果随机选取的样本点不理想,均值点很可能会落到 local optima,如下图所示:
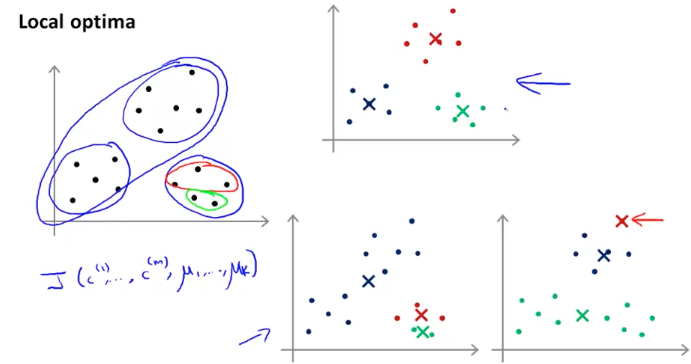
为了避免这种情况出现,我们可以尝试多次计算:
For i = 1 to 100 {
-
Randomly initialize K-means.
-
Run K-means. Get $c^{(1)},…,c^{(m)},…,\mu_{1},…,\mu_{k}$
-
Compute cost function(distortion) $J(c^{(1)},…,c^{(m)},…,\mu_{1},…,\mu_{k})$
}
4 . Pick clustering that gave lowest cost $J(c^{(1)},…,c^{(m)},…,\mu_{1},…,\mu_{k})$
维数约减 Dimensionality Reduction
对于多维度的样本数据我们希望可以将其缩减到低维度,这样可以对数据进行可视化处理,便于观察和理解数据。例如将二维数据映射到一维,3 维数据映射到二维,映射过程主要是通过投影完成
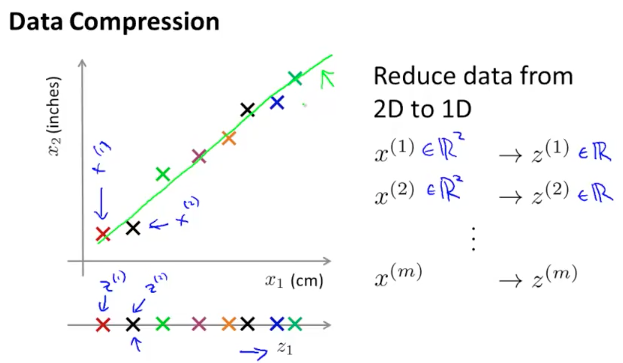
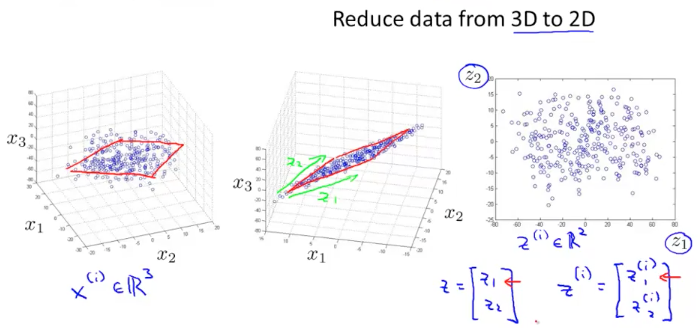
一种常用的降维算法叫做主成分分析PCA( Principal Component Analysis),它可以将$n$维数据映射成$k$维数据。具体来说,是找到$k$个向量$u^{(1)},u^{(2)},…,u^{(k)}$,使各个数据点在该向量上的投影误差(距离)最小。通俗的说,PCA 就是尝试寻找一个低维平面将高维度数据投影到这个平面,且各个点到该平面的垂直距离最短(误差最小)
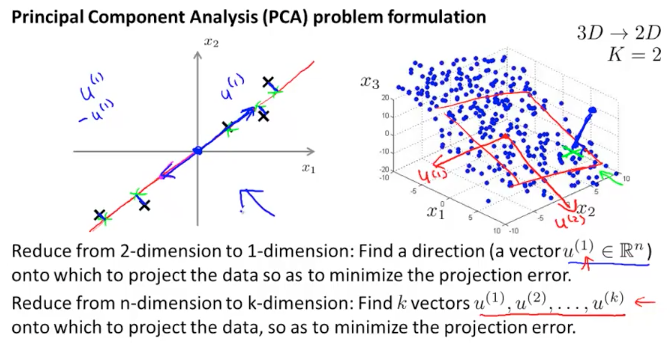
在使用 PCA 之前,通常要对数据进行预处理,使样本保持在统一数量级上。假设有训练样本:${x^{(1)}, x^{(2)},…,x^{(m)} }$,对其进行 feature scaling(mean normalization):
\[\mu_{j}=\frac{1}{m} \sum_{i=1}^{m} x_{j}^{(i)}\]接下来要解决两个问题,一是怎么计算投影平面$[u^{(1)},u^{(2)},…,u^{(k)}]$,而是怎么计算平面中的点
- 我们定义投影平面为$U_{\text{reduce}}$,维度为:nxk
- 平面中的点构成的矩阵为$Z$维度为 kx1
第一步先计算协方差矩阵得到 sigma 矩阵$\sum$
\[\sum=\frac{1}{m} \sum_{i=1}^{m}(x^{(i)})(x^{(i)})^{T}\]向量化实现为:
\[\Sigma=\frac{1}{m} \cdot X^{T} \cdot X\]其中$x^{(i)}$为$n \times 1$矩阵,因此$\sum$ 为 $n \times n$矩阵。
第二步计算$\sum$的特征值和特征向量,Octave 可直接使用 svd 函数对矩阵进行奇异值分解:
[U,S,V] = svd(Sigma)
在返回的三个结果中,$U$为 nxn 矩阵,我们从中取出前$k$列,得到$U_{\text{reduce}}$矩阵,既是我们想要的投影平面
第三步计算$Z$矩阵:
\[Z=U_{\text{reduce}}^{T} \cdot X\]其中,$U_{\text{reduce}}^{T}$为 kxn 的矩阵,x 为 nx1 的矩阵,因此$Z$为 kx1 的矩阵
总结一下上述过程的 Octave 实现为:
Sigma = (1/m) * X'*X;
[U,S,V] = svd(Sigma);
Z = zeros(size(X, 1), K);
U_reduce = U(:, 1:K);
for i=1:size(X,1)
x = X(i, :)';
Z(i,:) = x' * U_reduce;
end
这部分涉及到一些的数学推导,需要理解矩阵的特征值,特征向量,奇异值分解以及协方差矩阵的物理意义等等,此处暂时忽略这些概念,把 PCA 当做黑盒来看待
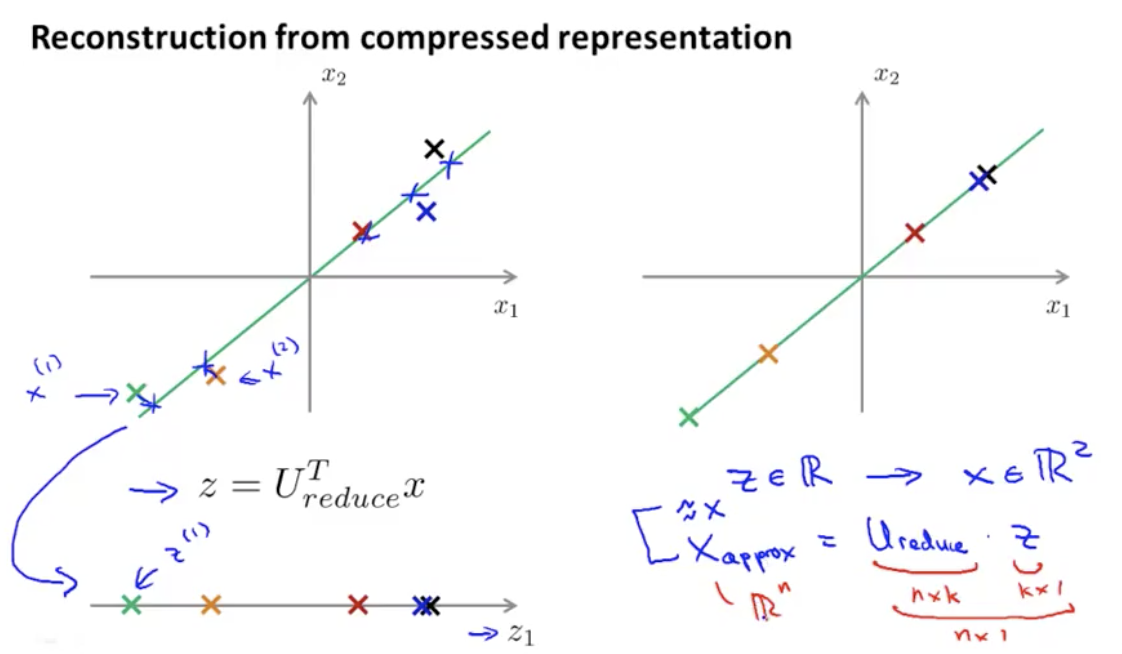
当我们有了低维度的$Z$,如何还原出高维度的$X$,可通过如下式子:
\[X_{\text{approx}}=U_{\text{reduce}}^{T} \cdot Z\]这里,$U_{\text{reduce}}^{T}$是 nxk 的,$Z$是 kx1 的,$X_{\text{approx}}$是 nx1 的, matlab 实现为:
function X_rec = recoverData(Z, U, K)
X_rec = zeros(size(Z, 1), size(U, 1));
for i=1:size(Z,1)
v=Z(i,:)';
X_rec(i,:)=v' * U(:, 1:K)';
end
end
接下来的问题是如何选择$k$值,使用下面公式:
\[\frac{\frac{1}{m} \sum_{i=1}^{m} \|x^{(i)}-x_{\text{approx}}^{(i)} \|^{2}}{\frac{1}{m} \sum_{i=1}^{m} \|x^{(i)} \|^{2}} \le 0.01 \quad(1%)\]其中,分子为样本平均投影误差的平方和,分母为样本数据的平均方差和,选取最小的$k$值,使比值小于等于 0.01。这个式子的意思是“在保留了 99%的样本差异性的前提下,选择了 K 个主成分”,具体的做法如下:
- 选取$k=1$
- 计算$U_{\text{reduce}},z^{(1)},z^{(1)}…,z^{(m)},x_{\text{approx}}^{(1)},…,x_{\text{approx}}^{(m)}$
- 检查上述式子结果是否满足条件,如果不满足,重复第一步令$k=k+1$
如果使用 Octave,在[U,S,V] = svd(Sigma); 的返回值中,S矩阵是一个对角阵,我们可以用这个矩阵简化对$k$值的计算:对于给定的任意$k$值,计算
通常情况下选取$k=1$,缓慢增大$k$值,观察上面式子计算结果。这种方式的好处是只需要计算一次svd得到$S$即可,比较高效
